Científicos de la Universidad de Stanford han descubierto que DRT3, un sistema de defensa único presente en las bacterias, crea ADN para proteger contra las infecciones virales. DRT3 está compuesto por dos enzimas diferentes llamadas transcriptasas inversas, Drt3a y Drt3b, y un fragmento de ARN no codificante (ARNnc). Juntos, estos tres elementos forman una larga cadena de ADN bicatenario con repeticiones alternas (GT/AC).
Las dos proteínas, Drt3a y Drt3b, utilizan estrategias diferentes para sintetizar las dos hebras complementarias de ADN. Drt3a sigue el método habitual de copiar una secuencia específica y conservada de ácidos nucleicos, en este caso ACACAC, que se encuentra integrada en el ARN no codificante del sistema como su modelo.
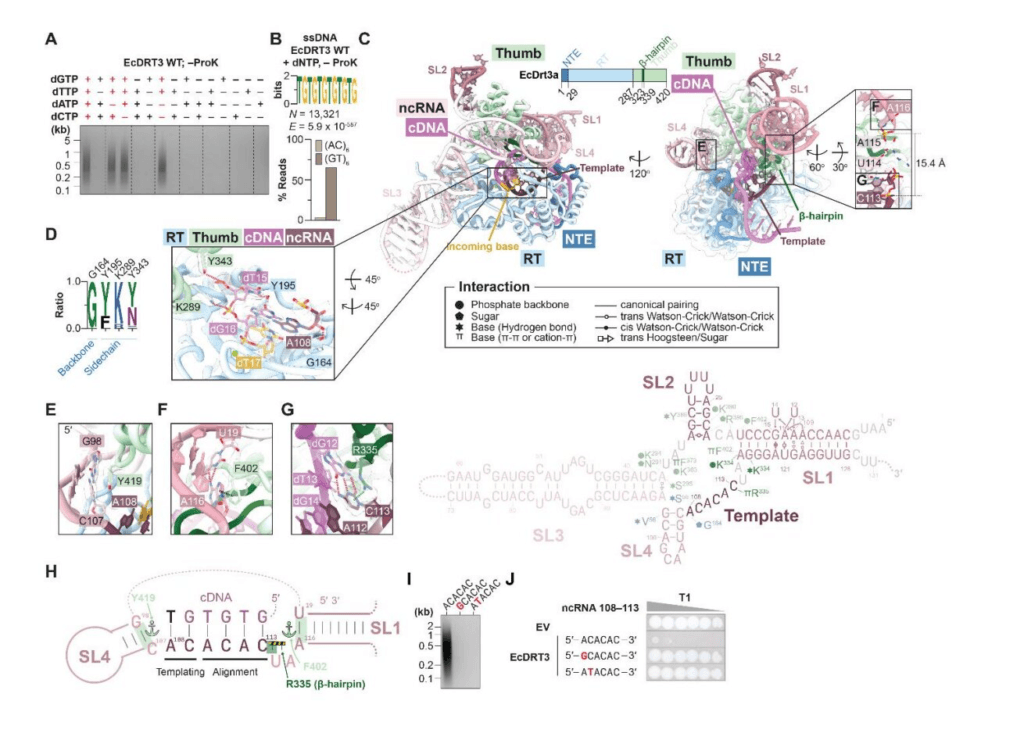
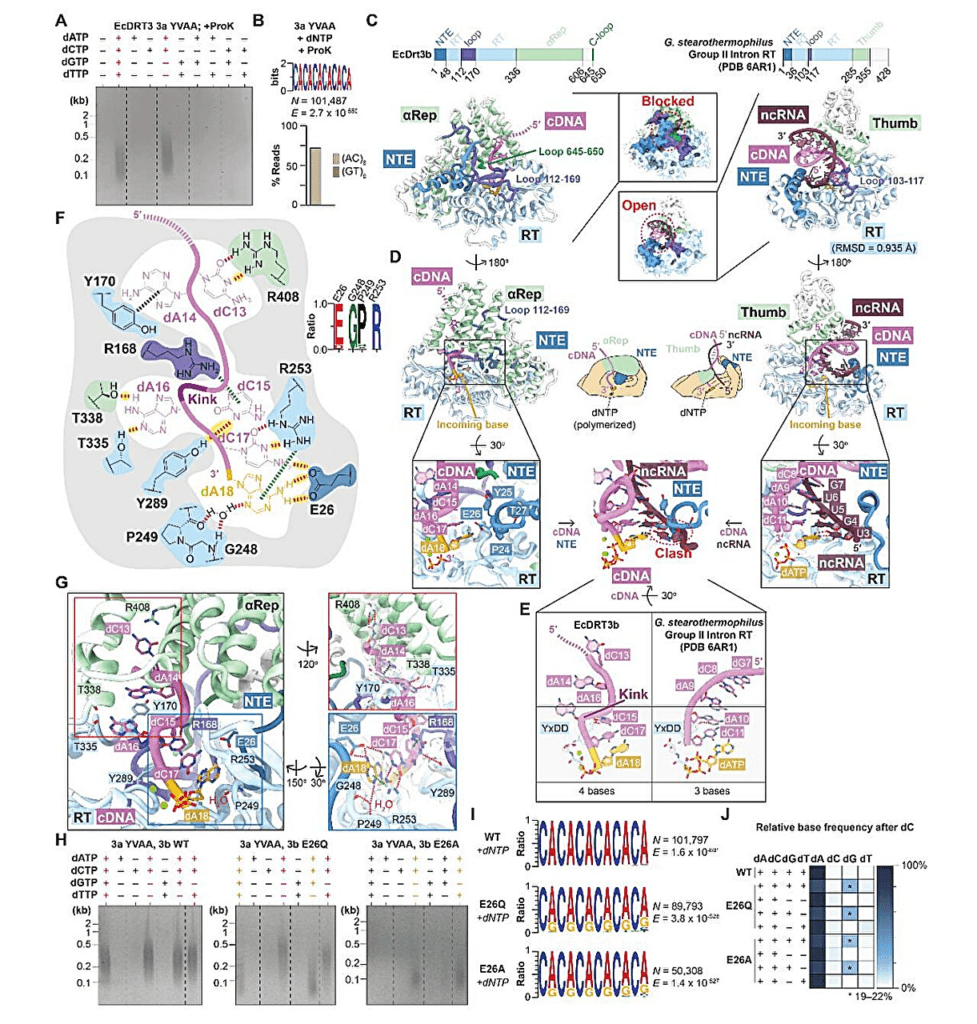
Al leer directamente esta plantilla de ARN, produce la cadena de ADN poli(GT) correspondiente. Lo más destacable del estudio fue el método de plantilla proteica previamente desconocido utilizado por Drt3b. No necesita una plantilla de ácido nucleico para construir la segunda cadena. En cambio, utiliza su propia estructura proteica como molde para asegurar que los bloques de construcción del ADN se agreguen en un orden preciso. Los resultados se publican en la revista Science.
Ensamblaje sin plantilla
Durante mucho tiempo, los científicos creyeron que las enzimas sólo podían sintetizar ADN y ARN siguiendo un ácido nucleico existente como plantilla o sin ninguna. Esto último generalmente resultaba en secuencias repetitivas o cortas y predecibles.
Científicos que estudian bacterias descubrieron que las transcriptasas inversas asociadas a la defensa (DRT) utilizan métodos sorprendentemente variados y hasta ahora desconocidos para sintetizar ácidos nucleicos que ayudan a las bacterias a resistir las infecciones virales. Sin embargo, no estaba claro si las bacterias podían usar las DRT para sintetizar ADN complejo y con secuencias específicas sin una plantilla de ácido nucleico y, de ser así, qué mecanismos estaban involucrados. En este estudio, el equipo comenzó su investigación analizando los códigos genéticos de miles de cepas bacterianas en busca de sistemas DRT3.
Lo encontraron en al menos 20 especies bacterianas diferentes, donde las proteínas Drt3a y Drt3b casi siempre aparecen juntas. Para comprobar la función del sistema, introdujeron la proteína DRT3 en bacterias E. coli y las expusieron a diversos fagos o virus. El mecanismo de defensa logró eliminar al enemigo. Sin embargo, el sistema no funcionaba de forma continua y sólo se activaba al detectar ST61, una proteína específica codificada por virus.
El equipo realizó una secuenciación de ADN para identificar qué se estaba produciendo exactamente. Observaron largas cadenas repetitivas de ADN bicatenario con un patrón alternante muy específico.
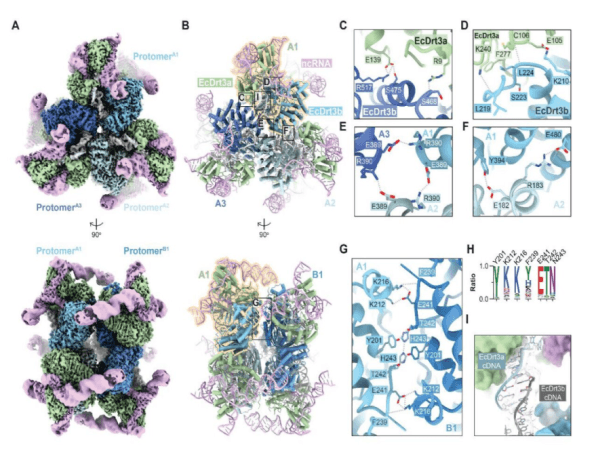
Las imágenes 3D de alta resolución producidas mediante microscopía crioelectrónica (crio-EM) revelaron que DRT3 es una entidad altamente organizada, compuesta por seis proteínas Drt3a, seis proteínas Drt3b y seis ARN no codificantes, unidos en un hexámero simétrico, una molécula compuesta por seis monómeros idénticos. La vía metabólica recientemente descubierta, mediada por proteínas y utilizada en la defensa bacteriana, podría abrir nuevas posibilidades para la ingeniería de bacterias con fines biotecnológicos y médicos. Para seguir avanzando en este campo, futuras investigaciones deberán dilucidar cómo el ADN sintetizado interrumpe la invasión viral.
Fuente: Phys.org.